绘制人类基因组计划是世界上最大的科学合作之一。Completing the full genome sequencing for "the book of life“在1000名科学家的努力和30亿美元的预算下,花了10多年时间。这个庞大的项目完成20年后,由于更先进的测序工具,现在可以在8天内以1000美元左右的价格完成一个完整的人类基因组测序。由于基因组测序领域已被更多的应用所接受,因此今天仍有必要进一步改进基因组测序工具,包括法医学,疾病建模与识别,以及个性化药物(例如,识别导致药物在一个病人身上起作用而在另一个病人身上起作用的基因)。
最初的测序技术依赖于标准的DNA电泳技术,如平板凝胶和毛细管,allowing for the preparation of only small numbers of samples at a time.这个样品制备限制是人类基因组计划期间成本和加工时间增加的主要原因。在过去的几十年中,许多工作都致力于改进样品制备技术。作为第一步,电泳技术已经优化到boost the sample throughputwith user-friendly,更小,以及功能平台。Traditional DNA separation gels,几十年来一直是金本位,已经被微制作的柱状阵列和纳米尺度的确定性横向位移阵列所取代。
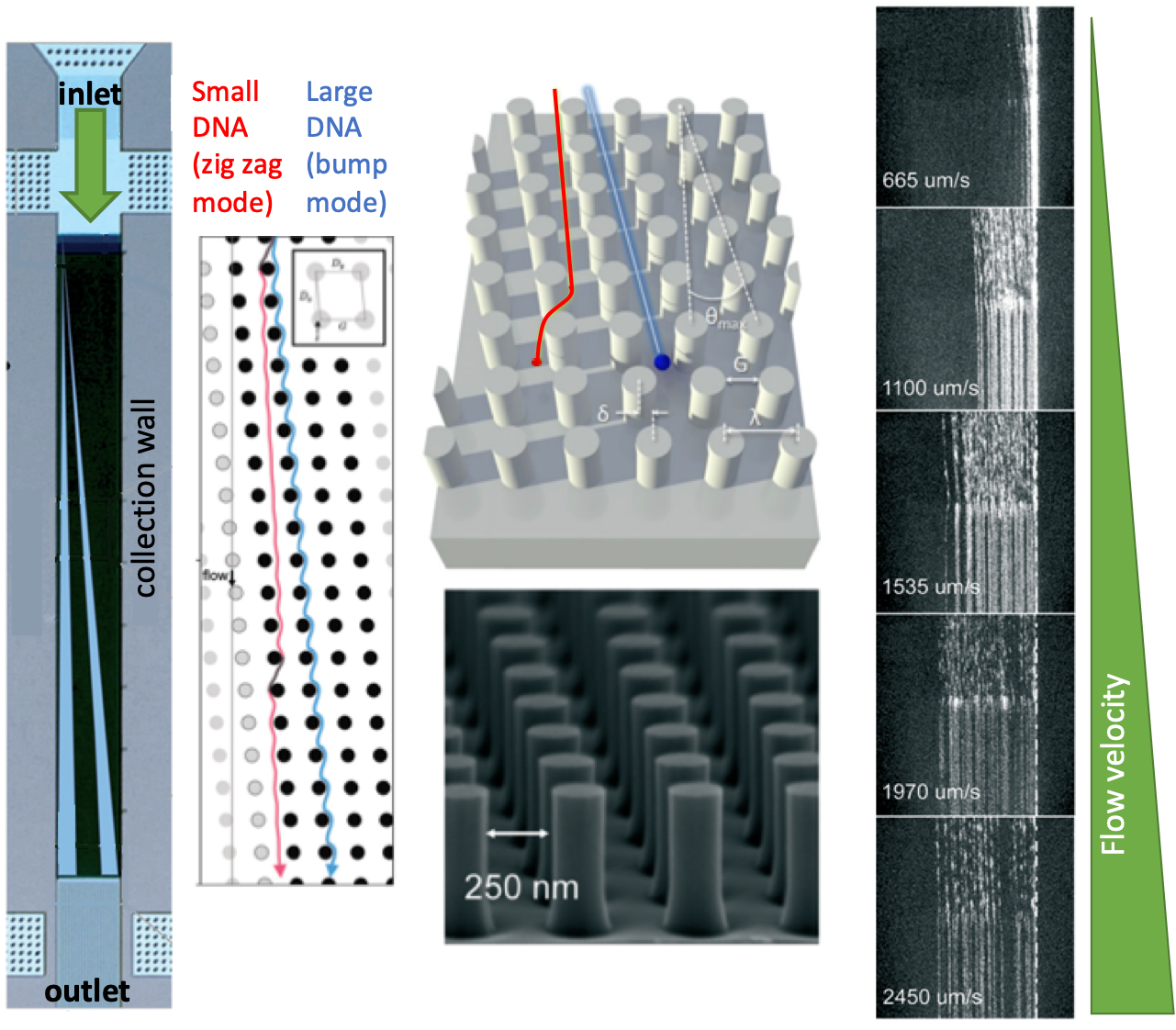
IBM T.J.的研究人员最近展示了纳米级确定性横向位移阵列的一个很好的例子。纽约西奈山沃森研究中心和伊坎医学院,美国。在这项工作中,研究人员将DNA分为100-10000个碱基对,大小选择分辨率为200个碱基对。为了实现这一目标,在硅片上制作了四种不同的微芯片结构,其中阵列和纳米柱的尺寸针对每种配置进行了调整,以获得所选范围的DNA片段的最佳分离性能。每种配置都包含几个单独的阵列,以便在一个芯片中进行独立运行。不是施加电场,研究人员用压力驱动力把碎片分开。该策略尤其适用于在不受缓冲条件影响的情况下分离非带电物种(例如,离子强度)。
| 分离机理在纳米尺度上,确定的侧向位移阵列很简单:如果DNA片段的大小大于支柱的直径,碎片以大角度偏向收集墙,也称为通气模式。如果DNA片段的大小小于柱子的直径,碎片以名义上为零的角度移动,称为之字形模式。在这样一个系统中,diffusion of DNA fragments lead to intermediate migration angles,称为partial-bump mode。由于不同模式的存在,不同大小的DNA片段可以在阵列中分离,因为片段将遵循不同的轨迹。图1总结了分离机制,并给出了纳米级确定性横向位移阵列的轮廓。 |
在纳米尺度的确定侧向位移阵列中,间隙尺寸仅从微尺度调整到纳米尺度,如果不使用任何其他能改变DNA扩散行为的分子,离子强度(改变有效间隙距离)。在这样的环境下,研究人员发现,for the first time,不同碎片长度的流速相关性。主要是,在不同的DNA片段的给定大小范围内,改变流速会导致凹凸模式和之字形模式之间的转换:缓慢的速度会导致部分凹凸模式,而高速则会导致所有DNA片段的折叠成之字形。The nanometer-scale deterministic lateral displacement array could also be used as a purification tool with 75% recovery and 3-fold concentration enhancement of DNA fragments.该工具可以有效地用于准备下一代序列库,芯片内DNA鉴定,以及循环DNA表征应用。
下载免费的完整文章*单击下面的链接:
Gel-on-a-chip: continuous,基于纳米尺度横向位移的速度依赖性DNA分离
本杰明H。乌恩施,金成哲,Stacey M.吉福德,雅恩·阿斯蒂尔,王超,罗伯特L。布鲁斯Jyotica V.帕特尔伊丽莎白A。Duch,西蒙·道斯,Gustavo Stolovitzky和Joshua T.史密斯,实验室芯片,2018,芯片上的实验室文章
DOI:10.1039/C8LC01053F
布尔库古木苏is a researcher in Mesoscale Chemical Systems Group at the University of Twente in the Netherlands.她的研究兴趣包括开发用于单细胞蛋白质定量分析的微流体装置,下一代测序,芯片研究的分区器官,and desalination of water on the microscale.